TLDR; Odpověď: Mohli byste považovat tento konkrétní zbytek za jeden z obou konstrukčních prvků, ale je to složité volání a záleží na způsobu přiřazení sekundární struktury.
Nejednoznačná alokace sekundární struktury přichází poměrně často. I když je zřejmé, že jen málo lidí bude moci tento protein konkrétně použít, níže uvedený přístup by mohl být užitečný pro jiné proteiny.
Výchozí přiřazení pymolu
V PyMolu jsem použil fetch 1ae9 a zvýrazněno M na pozici 255 na řetězu A červeně. Chápu, proč to není uspokojivé vyjádření: alokace listu beta je velmi krátká a dotyčný zbytek je zjevně začátkem šroubovice.
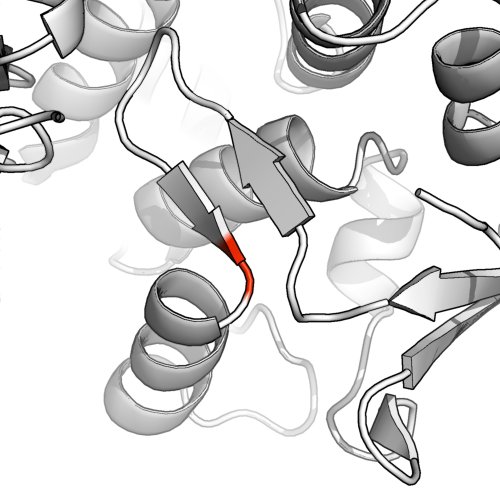
DSS je konzervativnější
Chcete-li spustit konzervativnější přidělení sekundární struktury, spusťte dss v pymolu (zředěném dssp). To ukazuje, že listy beta byly ve skutečnosti docela domnělé.

Vidíme proč, když se podíváme na model stick (níže). V blízkosti je jen několik (2–4) párů zbytků, které by byly k dispozici pro vodíkové vazby, a to i za předpokladu, že všechny 4 formy H-vazeb, které lze označit jako bona fide beta list, lze považovat trochu velkorysý.

Duální přiřazení může být v pořádku.
Při pohledu na tento příklad (1ae9) vidíme potenciál pro H-vazbu s dalším domnělým beta listem, stejně jako úhel páteře, který začíná tvořit spirálu. Je to klasický případ dvojznačného dvojího přiřazení. @AlexanderDScouras vyvozuje rozumný závěr, že obojí je v pořádku, a k přímému zodpovězení otázky: dvojí přiřazení je možné a povolené . V tomto konkrétním případě bych raději vyloučil beta listy, ale pod podmínkou, že jeden zdůrazňuje, že ve vlásenkové smyčce je spousta vodíkových vazeb.
Pokud je to rozumné.
Pokud můžete úkol rozumně zdůvodnit, je to pravděpodobně v pořádku. Můžete ručně přiřadit libovolný zbytek a sekundární strukturu.
# nastavit zbytek 155 na alfa-helikalter 155 /, ss = 'H' # aktualizovat scénu v PyMOL aby odrážel changes.rebuild
Důkazy jsou vždy dobrým nápadem pro podporu ručních přiřazení. Rychlým a důkladným způsobem by bylo spustit sekvenci pomocí několika prediktorů sekundární struktury nebo použít metaserver genesilico a ušetřit si tak nějaké potíže (budete potřebovat účet) ( toto se cítí jako byste se vrátili o krok zpět, protože nyní máte strukturu, takže buďte opatrní - pokud predikce sekvence nevypadá správně podle struktury, pravděpodobně to nebude ). Jinou metodou, kterou navrhuje shigeta, je spuštění této metody pomocí Ramachandranského spiknutí (oblíbená je RAMPAGE.)

Pokud je velmi nejasné, proberte to důkladně a jasně, kdykoli je tato část proteinu relevantní. Tato přiřazení sekundární struktury mají nakonec poněkud libovolné mezní hodnoty, a když se věci přiblíží prahovým hodnotám, je důležité přistupovat k situaci s jasností a konkrétností.
Zdroj obrázku pozemku Ramachandran: Autor Dcrjsr - vlastní práce, CC BY 3.0, https://commons.wikimedia.org/w/index.php?curid=9105708